Iris データセットの次元削減(t-SNE, Isomap, Spectral Embedding, LLE, kernel approximation 法)(Python, scikit-learn を使用)
1. サマリー
本記事では,Iris データセットの4次元特徴量を2次元に変換し,散布図で可視化する.使用する次元削減手法は,t-SNE,Isomap,Spectral Embedding,Locally Linear Embedding (LLE),kernel approximation(RBFSampler),PCA の6種類であり,いずれも Python の scikit-learn で実装する.
t-SNE,Isomap,Spectral Embedding,LLE は非線形手法であり,scikit-learn の manifold モジュールに含まれる.kernel approximation は RBF カーネルの近似特徴マップを利用する手法であり,kernel_approximation モジュールに含まれる.PCA は線形手法であり,非線形手法との比較に用いる.scikit-learn の cheat sheet によれば,Isomap や Spectral Embedding で十分な結果が得られないときは LLE が候補になり,データ数が 10000 以上のときは kernel approximation が候補になる.
2. 前準備(必要ソフトウェアの入手)
ここでは、最低限の事前準備について説明する。機械学習や深層学習を行う場合は、NVIDIA CUDA、Visual Studio、Cursorなどを追加でインストールすると便利である。これらについては別ページ https://www.kkaneko.jp/cc/dev/aiassist.htmlで詳しく解説しているので、必要に応じて参照してください。
Python 3.12 のインストール(Windows 上) [クリックして展開]
以下のいずれかの方法で Python 3.12 をインストールする。Python がインストール済みの場合、この手順は不要である。
方法1:winget によるインストール
管理者権限のコマンドプロンプトで以下を実行する。管理者権限のコマンドプロンプトを起動するには、Windows キーまたはスタートメニューから「cmd」と入力し、表示された「コマンドプロンプト」を右クリックして「管理者として実行」を選択する。
winget install --id Python.Python.3.12 -e --scope machine --silent --accept-source-agreements --accept-package-agreements --override "/quiet InstallAllUsers=1 PrependPath=1 Include_test=0 Include_pip=1 Include_launcher=1 InstallLauncherAllUsers=1 TargetDir=\"C:\Program Files\Python312\""
powershell -Command "$p='C:\Program Files\Python312'; $s=\"$p\Scripts\"; $m=[Environment]::GetEnvironmentVariable('Path','Machine'); if($m -notlike \"*$s*\") { [Environment]::SetEnvironmentVariable('Path', \"$p;$s;$m\", 'Machine') }"--scope machine を指定することで、システム全体(全ユーザー向け)にインストールされる。このオプションの実行には管理者権限が必要である。インストール完了後、コマンドプロンプトを再起動すると PATH が自動的に設定される。
方法2:インストーラーによるインストール
- Python 公式サイト(https://www.python.org/downloads/)にアクセスし、「Download Python 3.x.x」ボタンから Windows 用インストーラーをダウンロードする。
- ダウンロードしたインストーラーを実行する。
- 初期画面の下部に表示される「Add python.exe to PATH」に必ずチェックを入れてから「Customize installation」を選択する。このチェックを入れ忘れると、コマンドプロンプトから
pythonコマンドを実行できない。 - 「Install Python 3.xx for all users」にチェックを入れ、「Install」をクリックする。
インストールの確認
コマンドプロンプトで以下を実行する。
python --versionバージョン番号(例:Python 3.12.x)が表示されればインストール成功である。「'python' は、内部コマンドまたは外部コマンドとして認識されていません。」と表示される場合は、インストールが正常に完了していない。
AIエディタ Windsurf のインストール(Windows 上) [クリックして展開]
Pythonプログラムの編集・実行には、AIエディタの利用を推奨する。ここでは、Windsurfのインストールを説明する。Windsurf がインストール済みの場合、この手順は不要である。
管理者権限のコマンドプロンプトで以下を実行する。管理者権限のコマンドプロンプトを起動するには、Windows キーまたはスタートメニューから「cmd」と入力し、表示された「コマンドプロンプト」を右クリックして「管理者として実行」を選択する。
winget install --scope machine --id Codeium.Windsurf -e --silent --disable-interactivity --force --accept-source-agreements --accept-package-agreements --custom "/SP- /SUPPRESSMSGBOXES /NORESTART /CLOSEAPPLICATIONS /DIR=""C:\Program Files\Windsurf"" /MERGETASKS=!runcode,addtopath,associatewithfiles,!desktopicon"
powershell -Command "$env:Path=[System.Environment]::GetEnvironmentVariable('Path','Machine')+';'+[System.Environment]::GetEnvironmentVariable('Path','User'); windsurf --install-extension MS-CEINTL.vscode-language-pack-ja --force; windsurf --install-extension ms-python.python --force; windsurf --install-extension Codeium.windsurfPyright --force"--scope machine を指定することで、システム全体(全ユーザー向け)にインストールされる。このオプションの実行には管理者権限が必要である。インストール完了後、コマンドプロンプトを再起動すると PATH が自動的に設定される。
【関連する外部ページ】
Windsurf の公式ページ: https://windsurf.com/
必要なライブラリのインストール [クリックして展開]
管理者権限のコマンドプロンプトで以下を実行する。管理者権限のコマンドプロンプトを起動するには、Windows キーまたはスタートメニューから「cmd」と入力し、表示された「コマンドプロンプト」を右クリックして「管理者として実行」を選択する。
python -m pip install -U pip setuptools numpy pandas matplotlib seaborn scikit-learn scikit-learn-intelex
3. 実行のための準備とその確認手順(Windows 前提)
3.1 プログラムファイルの準備
本記事のプログラムは Jupyter Notebook 形式でセルごとに逐次実行する構成である.第5章のソースコードを順番にセルへ入力して実行する.Windsurf 等のエディタで Jupyter Notebook を新規作成し,iris_dim_reduction.ipynb として保存する(文字コード:UTF-8).
3.2 実行コマンド
Windsurf や Jupyter Notebook の GUI からセルを順に実行する.コマンドプロンプトから起動する場合は,ファイルの保存先ディレクトリに移動し,以下を実行する.
jupyter notebook iris_dim_reduction.ipynb3.3 動作確認チェックリスト
| 確認項目 | 期待される結果 |
|---|---|
| Iris データセットの読み込み | iris.head() で sepal_length, sepal_width, petal_length, petal_width, species の5列が表示される |
| データの形と次元の確認 | iris.shape が (150, 5),iris.ndim が 2 を返す |
| 0, 1, 2, 3 列目の表示 | iris.iloc[:, 0:4] で 150 行 × 4 列の数値データが表示される |
| t-SNE による次元削減 | 2次元配列が出力され,3種の花が色分けされた散布図が表示される |
| Isomap による次元削減 | 同上 |
| Spectral Embedding による次元削減 | 同上 |
| LLE による次元削減 | 同上 |
| kernel approximation による次元削減 | 同上 |
| PCA による次元削減 | 同上 |
4. 概要・使い方・実行上の注意
4.1 Iris データセット
Iris データセットは seaborn の load_dataset 関数で読み込む.サイズは 150 × 5,次元数は 2 である.最後の列 species は花の種類を表すラベルデータである.次元削減の対象は 0~3 列目(sepal_length, sepal_width, petal_length, petal_width)の4つの数値特徴量であり,これを2次元に変換して散布図で可視化する.
4.2 散布図プロット関数
各手法の結果を可視化するため,共通の関数 scatter_label_plot を定義する.変換後の行列 M の先頭2列を散布図にプロットし,ラベル b で色分けする.
4.3 各次元削減手法
t-SNE:sklearn.manifold.TSNE を使用する.n_components=2 を指定し,fit_transform で変換する.
Isomap:sklearn.manifold.Isomap を使用する.n_components=2, n_neighbors=10 を指定し,fit_transform で変換する.
Spectral Embedding:sklearn.manifold.SpectralEmbedding を使用する.n_components=2, n_neighbors=10 を指定し,fit_transform で変換する.
LLE:sklearn.manifold.LocallyLinearEmbedding を使用する.n_components=2, n_neighbors=10 を指定し,fit_transform で変換する.scikit-learn の cheat sheet によれば,Isomap や Spectral Embedding で十分な結果が得られないときの候補である.
kernel approximation:sklearn.kernel_approximation.RBFSampler を使用する.gamma=1, n_components=2 を指定し,fit_transform で2次元に写像する.scikit-learn の cheat sheet によれば,データ数が 10000 以上のときの候補である.
PCA(線形手法との比較):上記はいずれも非線形手法である.比較のため,線形手法である PCA(主成分分析)を用いる.PCA は分散が最大となる方向に射影する手法である.sklearn.decomposition.PCA を使用し,n_components=2 を指定する.
5. ソースコード
5.1 Iris データセットの読み込み
import pandas as pd
import seaborn as sns
sns.set()
iris = sns.load_dataset('iris')

5.2 データの確認
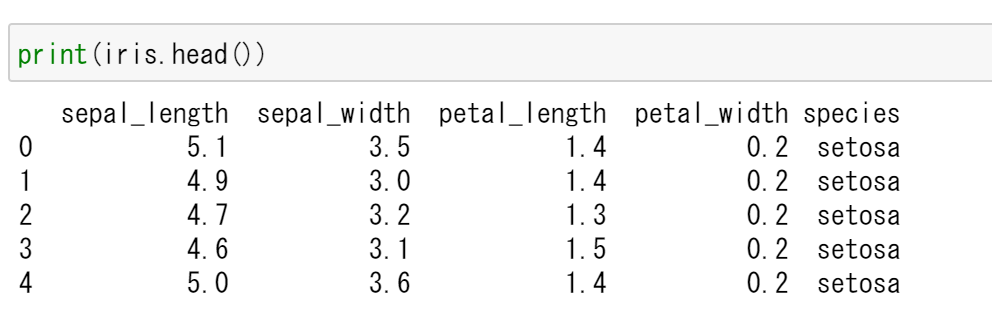
print(iris.head())
5.3 形と次元の確認
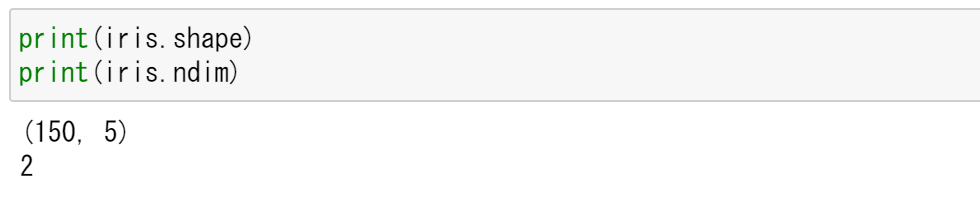
print(iris.shape)
print(iris.ndim)
5.4 Iris データセットの 0, 1, 2, 3 列目の表示
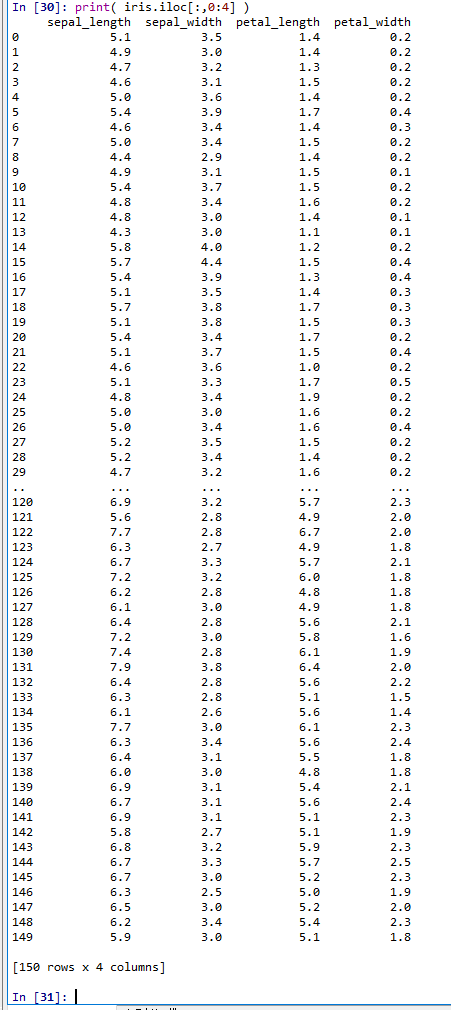
print( iris.iloc[:,0:4] )
5.5 散布図プロット関数の定義
import numpy as np
%matplotlib inline
import matplotlib.pyplot as plt
def scatter_label_plot(M, b, alpha):
a12 = pd.DataFrame(M[:, 0:2], columns=['a1', 'a2'])
f = pd.factorize(b)
a12['target'] = f[0]
g = sns.scatterplot(x='a1', y='a2', hue='target', data=a12, palette=sns.color_palette("hls", np.max(f[0]) + 1), legend="full", alpha=alpha)
for i, label in enumerate(f[1]):
g.legend_.get_texts()[i].set_text(label)
plt.show()
5.6 t-SNE 法による次元削減
from sklearn.manifold import TSNE
d = TSNE(n_components=2).fit_transform(iris.iloc[:, 0:4])
print(d)
scatter_label_plot(d, iris.iloc[:, 4], 1)
5.7 Isomap 法による次元削減
from sklearn.manifold import Isomap
d = Isomap(n_components=2, n_neighbors=10).fit_transform(iris.iloc[:, 0:4])
print(d)
scatter_label_plot(d, iris.iloc[:, 4], 1)
5.8 Spectral Embedding 法による次元削減
from sklearn.manifold import SpectralEmbedding
d = SpectralEmbedding(n_components=2, n_neighbors=10).fit_transform(iris.iloc[:, 0:4])
print(d)
scatter_label_plot(d, iris.iloc[:, 4], 1)
5.9 LLE 法による次元削減
from sklearn.manifold import LocallyLinearEmbedding
d = LocallyLinearEmbedding(n_components=2, n_neighbors=10).fit_transform(iris.iloc[:, 0:4])
print(d)
scatter_label_plot(d, iris.iloc[:, 4], 1)
5.10 kernel approximation 法による次元削減
from sklearn.kernel_approximation import RBFSampler
d = RBFSampler(gamma=1, n_components=2).fit_transform(iris.iloc[:, 0:4])
print(d)
scatter_label_plot(d, iris.iloc[:, 4], 1)
5.11 PCA 法による次元削減(線形手法との比較)
from sklearn.decomposition import PCA
d = PCA(n_components=2).fit_transform(iris.iloc[:, 0:4])
print(d)
scatter_label_plot(d, iris.iloc[:, 4], 1)
6. まとめ
t-SNE
TSNE で n_components=2 を指定し,4次元の Iris データを2次元に変換する.局所的な構造を保持する非線形手法である.
Isomap
Isomap で n_components=2, n_neighbors=10 を指定して次元削減を行う.測地線距離(データ点を近傍グラフ上でたどったときの最短経路距離)を保持する非線形手法である.
Spectral Embedding と LLE
SpectralEmbedding と LocallyLinearEmbedding をそれぞれ n_components=2, n_neighbors=10 で使用する.scikit-learn の cheat sheet によれば,Isomap や Spectral Embedding で十分な結果が得られないときは LLE が候補になる.
kernel approximation
RBFSampler で gamma=1, n_components=2 を指定し,RBF カーネルの近似特徴マップで2次元に写像する.scikit-learn の cheat sheet によれば,データ数が 10000 以上のときに候補となる.
PCA(線形手法との比較)
非線形手法との比較のために PCA を使用する.分散が最大となる方向に射影する線形手法である.
![[kaneko lab.]](https://www.kkaneko.jp/info/logo_png.png)